ご利用の流れ
こちらのライトシート顕微鏡は九大の研究環境整備事業により導入されたもので、学内共通機器(教育・研究支援センター管理)となっていますが、顕微鏡の使用および解析の専門性が高いことから、当面の間、今井研にて利用のサポートを行います。初回の利用にあたっては、こちらのページをよく読んだ上で(特に、本当に共焦点ではなく、ライトシート顕微鏡で見るべきなのかをよく考えた上で)、今井(imai.takeshi.457[at]m.kyushu-u.ac.jp )もしくは秘書の野副(nozoe.emi.657[at]m.kyushu-u.ac.jp)までご連絡ください。その後、今井研担当者の方でコンサルテーションを行い、撮影の日程調整を行います。
2024年4月以降(予定)は支援センターに利用登録が必要になります。また、ShareAIDを通して利用料金の支払いが必要になります(1時間あたり1500円)。
教育・研究支援センター
の掲載ページはこちら。利用・登録方法についてはこちらをご確認ください。
ShareAID
のページはこちら。利用にあたっては、今井研担当者を通して下記のGoogle Calendarで予約を行い、紙ベースの使用簿を作成しますが、同時にShareAIDでも使用簿を付けて下さい。ShareAIDでの使用簿に基づき、毎月自動的に課金されます。
ShareAIDの登録・利用方法(簡易版)はこちら。
顕微鏡の仕様
こちらのライトシート顕微鏡(Miltenyi Biotec社Ultramicroscopy Blaze)は、臓器丸ごとの3D蛍光イメージングが可能な顕微鏡です。サイズの大きな透明化標本のイメージングに特化した機種となっています。
Objective lens:
1.1x (NA 0.1, WD 17 mm)
4x (NA 0.35, WD 16 mm)
12x (NA 0.53, WD 10.9 mm)
Dipping cap:
屈折率によって使い分けを行います。屈折率に関しては水(1.33)から有機溶媒(1.57)までカバーしているため、基本的にほとんどの透明化法に対応可能です。
water (RI 1.33-1.41)
CLARITY (RI 1.42-1.48)
DBE (RI 1.49-1.57)
Laser:
445, 488, 515, 561, 639 nm
青色(405)レーザーは透過率が悪いため搭載していません。このため、DAPIやBFPは使えません。核染色が必要な場合はRedDot2(639nm励起)を用いますが、全脳registrationに関しては自家蛍光を使えば十分なことがほとんどです。
Emission filter (中心、幅; nm):
480/40 (CFP)
510/20 (GFP narrow)
525/50 (GFP wide)
545/30 (YFP)
595/40 (RFP)
650/30 (mKate2, tdKatushka)
680/30 (AF647, RedDot2)
Camera:
2560 x 2160, QY max 60%
PC:
RAM 128 GB, HDD: 10TB x 1, 16 TB x 2, NVIDIA Quadro P1000(4GB)
サンプル駆動域(X,Y,Z):
24mm,50mm,23mm
光シート厚:
4-24 um
予約表(Google Calendar)
こちらのカレンダーは閲覧のみになっています。予約は今井研の担当者を通して行います。利用後はShareAIDのページを通して利用簿を付けて下さい。
撮像にあたっての注意点
データサイズが膨大となるため、とりあえず高解像度で臓器丸ごと撮像する、ということはオススメしません。高解像度で見たければ共焦点顕微鏡の方が良いです。実験の目的に合わせて実験をデザインすることが必須です。臓器丸ごとのデータになると、ご自分のPCでは画像が開けない可能性が高いです。
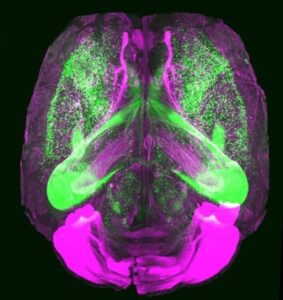
マウス全脳をとりあえず撮像する場合は1.1xレンズで撮像します(右の写真:この場合は画像のstitching不要、所要時間は1時間/チャンネル以内)。自動でレジストレーションと定量を行いたい場合は4xレンズで撮像(所要時間は半日程度/チャンネル)し、stitchingします。
神経突起まで観察したい場合は12xのレンズを使用。但し、12xで全脳画像を取得することはまず不可能なので、1.1xないし4xの画像に基づいて、見たい場所だけを撮像することが現実的です。
マウスの全脳をイメージングする場合のデータサイズの目安としては、1.1xレンズであれば数10GB/チャンネル、4xレンズであれば~500GB/チャンネル。12xレンズで全脳撮像することは現実的に不可能。データ解析にあたっては、データサイズ×3倍のメモリ(RAM)が必要なため、ハイスペックな専用の解析マシンが必要です。
当面はCUBIC-L/R(屈折率1.52)で運用する予定です。希望があれば、SeeDB2G(CLARITY)やBABBも対応可能ですが、対物レンズのdipping cap交換と光軸調整、撮像用オイルの交換が必要になります。
とりあえず臓器を丸ごと見たい場合、まずはCUBIC-L/Rを使用。CUBIC-Lは自作可能だが、CUBIC-R+ (M)は市販品(TCI, #T3741)を使用。蛍光タンパク質の輝度を最大限保持したい場合は、Scale-CUBIC1 (or CUBIC-L)で脱脂後、SeeDB2Gで透明化すると良い。蛍光タンパク質が褪色しても問題無く、CUBICでは透明度が不十分な場合は、3DISCO、BABB、ECiなど、有機溶媒系の透明化液を検討。特にヒト標本は有機溶媒系での実績が多い。
データ転送に時間が掛かるため、データを持ち出す際の外部記憶媒体は高速SSD(PCIe 3.0 or 4.0)のみとします。4TB程度が比較的安価で使いやすい。外付けHDDは非推奨。
プロトコル例
CUBIC-L/Rによるマウス全脳透明化プロトコル
Sample preparation
しばしば、お持ち頂いた全脳イメージング用のサンプルで自家蛍光が高いことがあります。これは灌流が不十分で血液が残っているためだと思われます。4% PFAで潅流固定する前に、PBS 10 mL程度で灌流し、十分に脱血することが重要です。
Delipidation with CUBIC-L
1. Take the sample and immerse it in 4% PFA at 4℃ for 24hr (with gentle shake)
2. Wash the sample with PBS, 1hr ×3 times at RT (with gentle shake)
3. Immerse the sample in CUBIC-L (30-40 mL in 50 mL tube) at 37℃ for 6 days (with shake)
(Replace the CUBIC-L with a new tube on Day 2 or 3 )
It’s not needed to exchange CUBIC-L every day. Shaking speed is important (e.g. reciprocating shaker for 50~100 rpm).
4. Wash the sample with PBS, RT, 2hr×3 times (with gentle shake)
Counterstaining
5. Dilute the Propidium Iodide (ex 532) or RedDot2 (ex 637) with the staining buffer
6. Immerse the sample in the antibody diluted staining buffer, RT for 4-5 days
7. Wash the sample with PBS 1 hr ×3 RT (with gentle shake)
Final Clearing for index matching
8. Immerse the sample in 10mL of 1/2-diluted CUBIC-R (diluted with miliQ) at RT for 5-10 h with shake (we recommend 50 mL tube)
9. Immerse the sample in 10mL of CUBIC-R at RT for 10h or overnight with shake (in 50 mL tube)
10. Exchange the CUBIC-R and shake overnight x3 times at RT (in 50 mL tube)
注意点:
10mLのCUBIC-RでRI matchingを行う場合、最低でも3回溶液を交換してovernight処理を繰り返す必要があります。サンプルを屈折率が1.52のオイルに沈めて撮像しますので、透明化サンプルの屈折率が完全に1.52にならないときれいな像が得られません。
CUBIC-L
1. Triton-X 50mL
2. N-Butyldiethanolamine (TCI, B0725) 50mL
3. dH2O 400mL
CUBIC-R+ (M)
TCI (T3741)
Staining buffer
500 mM NaCl-PBS
マウス全脳抗体染色
我々の方ではあまり経験がありませんが、抗体染色をする場合は有機溶媒系の透明化液の方が良いです。ミルテニー社のこちらの資料を参照してください。
フリーソフトを使った解析の流れ
顕微鏡本体では画像取得しか行えません。大量の画像の貼り合わせや定量など、解析は各自で行う必要があります。基本的にはImageJ/FijiやImarisを使用します。Imaris/Fijiはフリーソフトですが、Imarisは有料ソフトのため、共通機器等を使うことになります。可視化のみ可能なImaris Viewerはフリーですが、定量や動画作成をする場合は有料版が必要です。当研究室で行っているマウス全脳解析の流れは以下の通り。
取得した画像は、必要に応じてImageJ/FijiのBigStitcherで画像のstitchingを行う。画像の可視化はImaris Viewerを使用可能。binningとcoronal画像への変換を行った後、BIRDSで標準脳CCFv3への自動registrationを行う。解析PCのメモリは画像サイズの3倍以上は必要(最低128GB)なので注意。
共通機器室にもImarisがあるが、PCのメモリが128GBのため扱えるデータサイズに制限がある(binningによってデータサイズを減らさないと画像ファイルを開けない可能性がある)。今井研のImarisマシンは1.5TBのメモリを搭載しているので大容量データの解析も可能。
他の臓器に関してはノウハウが限られているので応相談となります。機械学習を使って対象物を自動検出する際にはilastikなども使っています。
謝辞の記載方法
こちらの機器は学内共通機器(教育・研究支援センター管理)となっておりますので、成果発表の際にはこちらの記載例に従って謝辞をお願いします。
サポート担当者に対する謝辞例:We thank xxx for technical help on light-sheet microscopy.
大量のサンプルの解析や、新しいデータ解析を必要とするサポートなど、共同研究ベースで進める場合は別途今井までご相談下さい。
お問い合わせ
現在、テストラン中です。画像取得や解析のサポート、共同研究のご相談は今井まで。学外については共同研究ベースでのみの受け入れます。学術変革領域の方はこちら(gakuhen.dynamic.brain@gmail.com)までご相談下さい。メールのやりとりはPIが直接、もしくはPIをCCに入れた上でお願いします。